”KEGG富集分析“ 的搜索结果
转录组数据分析之一,先介绍相关基础知识,其次用实际案例为基础,由浅入深介绍GO+KEGG富集分析全过程
KEGG数据库是一个关于通路的数据库。本教程为学习KEGG提供了一个很好的指导
以下是对KEGG/GO富集分析的简要介绍:KEGG富集分析:KEGG富集分析基于KEGG数据库,对基因集合中的基因进行功能注释和通路富集分析。通过将基因集合与KEGG数据库中的通路注释进行比较,可以确定哪些通路在给定基因...
在此章节以前,还有一个WGCNA的分析,你若需要可以看**WGCNA分析 | 全流程分析代码**SCI文章复现 | GEO文章套路,数据下载和批次效应处理差异分析和PPI网路图绘制教程在前的教程中,我们已经获得差异基因(2.4 差异...
Hoea 是一个用于分层本体富集分析的 Python 模块,它促进了任何桌面上的 GO(基因本体)/KO(KEGG Orthology)富集分析。
KEGG信号通路富集分析
标签: 数据库
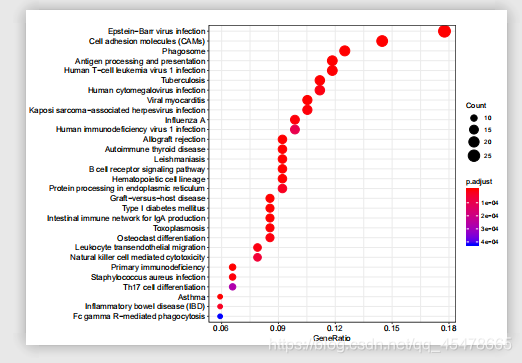
labs(x = "Gene Number", y = "",title = "Dotplot of Enriched KEGG Pathways", # 设置坐标轴标题及图标题。aes(x = Count,y = reorder(number,Count)))+ #横纵坐标及排序。color = expression(p.adjust),size = ...
GO和KEGG富集分析的注释信息(注释包) GO常用的注释信息包 GO的注释信息主要来自Bioconductor,提供了19个物种的org类型的GO注释信息。其中包括有常见的物种,如:牛、猪、人类、小鼠等。 BioconductorGO注释...
根据文章分析流程,将DEGs和WGNCA分析获得的结果去交集,获得的交集基因进行后续分析。我们在自己做分析时,或在写论文时,其实这些参数可以写进论文中,对读者是比较友好的。在差异分析中,我们获得600多个DEGs,在...
对于非模式生,可以先做KEGG注释,用注释文件直接进行计算,GO富集同理。 用到三个文件 1.背景基因的注释信息(所有可以注释到的基因),两列 2.ko的描述信息文件,两列 3.差异基因文件(软件会自动删掉没有注释到的...
GO and KEGG富集分析
标签: r语言
GO 基因本体涉及的基因和基因产物词汇分为三大类,涵盖生物学的三个方面: 细胞组分(cellular component)CC:细胞的每个部分和细胞外环境。 分子功能(molecular function)MF:可以描述为分子水平的活性(activity),如...
概念: GO是基因本体联合会所建立的数据库,旨在建立一个适用于各种物种的,对基因和蛋白质功能进行限定和描述的,并能随着研究不断深入而更新的语义词汇标准。GO 提供了一系列的语义...GSEA:基因集富集分析,用
前言:微博参与话题 #给你四年时间你也学不会生信#先前的富集分析教程本文主要针对非模式物种,但是有参考基因组可用1. R包安装及database下载# non-model, but have the genome> source(...
【代码】GO/KEGG富集分析(仅需基因列表)
pathway = read.table("kegg.result",header=T,sep="\t") pp = ggplot(pathway,aes(richFactor,Pathway)) #Pathwy是ID,richFactor是富集的基因数目除以背景的基因数目 # 改变点的大小 pp + geom_point(aes(size=R...
做过下游分析的小伙伴都知道富集分析的重要性,生信类文章大家总会在最后一步针对我们前面筛选出来的差异基因做一下GO/KEGG富集分析,研究一下他们参与到什么信号通路上或者参与什么生物学过程?富集分析的本质是...
推荐文章
- 反编译delphi_反编译Delphi(1/3)-程序员宅基地
- node_acl用法示例_node acl-程序员宅基地
- 使用STM32提供的DSP库进行FFT_stm32的dsp库 直流分量-程序员宅基地
- VScode 报错 :crbug/1173575, non-JS module files deprecated._crbug/1173575是什么原因-程序员宅基地
- C++学习_3-程序员宅基地
- eigen 构造变换矩阵(Eigen::Isometry3d或者Eigen::Matrix4d)的几种方式-程序员宅基地
- C++ 如何初始化静态类成员(静态成员必须在.cpp文件中初始化)_c++ 静态成员变量初始化-程序员宅基地
- 48,原子核物理实验方法篇_短时间的高剂量照射后果-程序员宅基地
- el-dialog修改默认内边距_el-dialog__body修改padding-程序员宅基地
- 公网下远程树莓派Raspberry Pi的SSH/WOL/监控/桌面的实现_ssh wol-程序员宅基地